Zentrosom-Dynamik
AG Mikeladze-Dvali
AG Mikeladze-Dvali

© Carolin Bleese
LSM - Graduate School Life Science Munich
Find us on Bluesky: tdvalilab.bsky.social
‚Ich hätte lieber Fragen, die nicht beantwortet werden können, als Antworten, die nicht hinterfragt werden können.‘
Richard Feynman
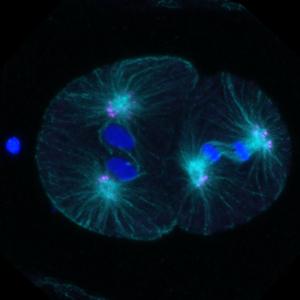
© Dvali lab
Die Zellteilung und die präzise Verteilung zellulärer Bestandteile auf zwei Tochterzellen sind grundlegend für alle lebenden Systeme. Zentrosomen sind die primären Keimungszentren für Mikrotubuli in tierischer Zellen, und steuern dadurch die Bildung einer bipolaren Spindel während der Zellteilung. Zentrosomen sind membranlose Organellen, die aus einem Paar Zentriolen bestehen, die in das Perizentrioläres Material (PCM) eingebettet sind. Die PCM ist eine hochdynamischen Proteinmatrix, deren Struktur und Zusammensetzung im Verlauf des Zellzyklus verändert. Sie ist gleichzeitig eine Plattform für regulatorische Proteine und mRNAs, die wiederum den Verlauf des Zellzyklus steuern. Fehlfunktionen zentrosomaler Komponenten sind mit zahlreichen menschlichen Erkrankungen verbunden, die von Mikrozephalie bis hin zu Krebs reichen, was die Notwendigkeit einer präzisen Regulation der Zentrosomdynamik und -biogenese unterstreicht.
Die Forschung in unserer Arbeitsgruppe wird von mehreren zentralen Fragen zur Zentrosomdynamik geleitet: Welche molekularen Mechanismen steuern den Umbau der Zentrosomen während des Zellzyklus? Wie kann ein membranloses Organell dynamisch bleiben und gleichzeitig den von Mikrotubuli erzeugten Zugkräften standhalten? Wie beeinflussen perizentrosomale Strukturen, wie zentrioläre Satelliten, die dynamischen Eigenschaften der Zentrosomen?
Eine generelle Neugier in fundamentalen Prozessen treibt unsere Forschung an, doch der Weg, dem wir folgen, ist stets voller Überraschungen!
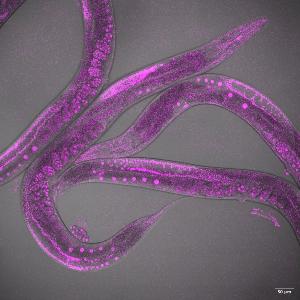
© Tamara Mikeladze-Dvali
Aufgrund seiner Eignung für genetische Manipulationen ist der Fadenwurm Caenorhabditis elegans unser bevorzugtes Modellsystem. Ein großer Vorteil von C. elegans liegt in seiner vergleichsweise einfachen Proteinzusammensetzung, während seine zentralen biologischen Signalwege hochgradig konserviert sind.
Wir nutzen C. elegans als ein Modell für Entwicklungsbiologie, wobei das Embryo für Live-Zell-Imaging im Fokus steht, da Prozesse hier räumlich und zeitlich präzise manipuliert werden können. Um die für uns relevanten Fragestellungen zu untersuchen, kombinieren wir verschiedene Ansätze, darunter quantitatives Live-Zell-Imaging, Molekularbiologie, Genetik und Biochemie
Schreiner A, Heim A, Pletschacher L, Alznauer LM, Schwenkert S, Wolff F, Zanin E, Mikeladze-Dvali T. PCMD-1 stabilizes the PCM scaffold and facilitates centriole separation. (2025) J Cell Biol. 2025 Dec 1;224(12):e202411107.
Lebedev M, Chan FY, Rackles E, Bellessem J, Mikeladze-Dvali T, Xavier Carvalho A, Zanin E. Anillin mediates unilateral furrowing during cytokinesis by limiting RhoA binding to its effectors. (2025) J Cell Biol. Jun 2;224(6):e202405182.
Stenzel L, Schreiner A, Zuccoli E, Üstüner S, Mehler J, Zanin E, Mikeladze-Dvali T. PCMD-1 bridges the centrioles and the pericentriolar material scaffold in C. elegans. (2021) Development. Oct 15;148(20):dev198416.
Erpf AC, Stenzel L, Memar N, Antoniolli M, Osepashvili M, Schnabel R, Conradt B, Mikeladze-Dvali T. PCMD-1 Organizes Centrosome Matrix Assembly in C. elegans. (2019) Curr Biol. 2019 Apr 22;29(8):1324-1336.e6.
von Tobel L, Mikeladze-Dvali T, Delattre M, Balestra FR, Blanchoud S, Finger S, et al. SAS-1 Is a C2 Domain Protein Critical for Centriole Integrity in C. elegans. (2014) PLoS Genet 10(11): e1004777.
Mikeladze-Dvali T, von Tobel L, Strnad P, Knott G, Leonhardt H, Schermelleh L, Gönczy P. Analysis of centriole elimination during C. elegans oogenesis. (2012) Development. May;139(9):1670-9.
Zakiah Talib (bis 2025)
Alina Schreiner (2026, post-doc in the S. Erçan lab, NYU, NYC)
Dr. Lisa Stenzel (2021, Group Leader/Project Manager, Microcoat Biotechnologie GmbH)
Dr. Anna Christine Erpf (2020, post-doc in L. Pelletier lab, Lunenfeld-Tanenbaum Research Institute, Toronto)
Lisa Marie Alznauer (2025)
Luisa Pletschacher (2025, PhD student at LMU Munich)
Disha Shenai (2024, PhD student at TU Dresden)
Nadja Bräuer (2023,PhD student at LMU Munich)
Kameshwari Tata (2022 Erasmus, PhD student at University College Dublin)
Alexander Schilder (2022)
Alexandra Degtyareva (2021, PhD student at MPI-CBG, Dresden)
Özgün Bahar (2021, PhD student at TU Dresden)
Alina Schreiner (2021, PhD student at LMU Munich)
Elisa Zuccoli (2021, PhD student at University of Luxemburg)
Sim Üstüner (2019, PhD student at University Giessen)
Martina Antoniolli (2018, PhD student at LMU Munich)
Christian Fischer (2016, PhD student at LMU Munich)
Carina Strasser (2015)
Mariam Osepashvili (2014, DAAD, PhD student at Ilia State University, Tbilisi)
Magherita Peron (2012-2013 Erasmus, PhD student at University of Padova)
Manuela Hefele (2013, PhD student at FAU Erlangen)
Jennifer Diehm (2013)
Erik Schmitt (2025)
Leo Hetzke (2024)
Felicia Haxel (2023)
Selina Cifci (2023)
Denise Ropertz (2022)
Judith Mehler (2018)
Annabel Kirgis (2015)
Marta Plotnikova (2015)
Mario Ernst (2015)
Andrea Lampp (2012)